Migliaia di pubblicazioni scientifiche e casi clinici peer-reviewed da consultare
Un team di scienziati internazionali ha recentemente identificato gli anticorpi ultrapotenti anti-sindrome respiratoria acuta grave coronavirus 2 (SARS-CoV-2) da donatori convalescenti.
Gli anticorpi sono in grado di neutralizzare una vasta gamma di varianti di SARS-CoV-2 anche a concentrazioni sub-nanomolari. Inoltre, le combinazioni di questi anticorpi riducono il rischio di generare mutanti di fuga in vitro. Lo studio è pubblicato sulla rivista Science.
Sfondo
Sindrome respiratoria acuta grave coronavirus 2 (SARS-CoV-2), l’agente patogeno causale della malattia da coronavirus 2019 (COVID-19), è un virus a RNA avvolto, senso positivo, a singolo filamento appartenente alla famiglia umana beta-coronavirus. La glicoproteina spike sull’involucro virale è composta da due subunità S1 e S2. Di cui, la subunità S1 si lega direttamente al recettore dell’enzima di conversione dell’angiotensina 2 (ACE2) della cellula ospite attraverso il dominio di legame del recettore (RBD) per avviare il processo di ingresso virale.
La maggior parte degli anticorpi terapeutici contro SARS-CoV-2 sono stati progettati sulla base della sequenza nativa della proteina spike trovata nel ceppo originale di Wuhan di SARS-CoV-2. Pertanto, nuove varianti virali con mutazioni multiple della proteina spike possono probabilmente sviluppare resistenza contro questi anticorpi. In questo contesto, gli studi hanno dimostrato che gli anticorpi sviluppati in risposta ai vaccini COVID-19 attualmente disponibili hanno meno efficienza nel neutralizzare le nuove varianti di preoccupazione (COV) di SARS-CoV, tra cui B.1.1.7, B.1.351, P1 e B.1.617.2.
Nel presente studio, gli scienziati hanno isolato e caratterizzato gli anticorpi RBD anti-spike dei pazienti guariti da COVID-19.
Identificazione degli anticorpi
Gli anticorpi sono stati isolati da quattro donatori convalescenti infettati dal ceppo Washington-1 (WA-1) di SARS-CoV-2. La sequenza di picchi nel ceppo WA-1 è simile alla sequenza di picco nel ceppo originale di Wuhan.
Le cellule B isolate da campioni di sangue derivati da donatori sono state ordinate per l’identificazione degli anticorpi. Ciò ha portato all’identificazione di quattro potenti anticorpi neutralizzanti che prendono di mira il picco RBD. Questi anticorpi hanno mostrato un’alta affinità per il picco sars-CoV-2 anche a concentrazioni nanomolari.
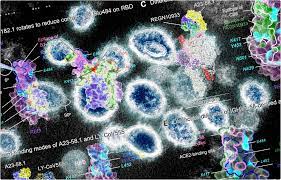
Per determinare se gli anticorpi ad alta potenza potessero bloccare ACE2 – spike binding, sono stati eseguiti test di interferometria ACE2-competition e cell surface binding. I risultati hanno rivelato che di 4 anticorpi, due legati a RBD nella “posizione verso l’alto” e due legati a RBD nella “posizione verso il basso”. Inoltre, tre anticorpi su quattro hanno bloccato direttamente l’interazione RBD – ACE2 e uno indirettamente ha inibito l’interazione attraverso l’ostacolo sterico – il rallentamento delle reazioni chimiche dovute alla massa sterica.
Neutralizzazione mediata da anticorpi
Tutti gli anticorpi sperimentali hanno mostrato una potenza significativamente più elevata nel neutralizzare le varianti contenenti mutazioni D614G rispetto al ceppo WA-1. Ulteriori analisi con particelle lentivirali pseudotipizzate con varianti spike hanno indicato che gli anticorpi mantengono un’elevata potenza nel neutralizzare un insieme diversificato di 10 varianti spike.
È importante sottolineare che tre anticorpi sperimentali su quattro hanno mostrato un’elevata efficacia nel neutralizzare 13 varianti circolanti di interesse / interesse di SARS-CoV-2, tra cui B.1.1.7, B.1.351, B.1.427, B.1.429, B.1.526, P.1, P.2, B.1.617.1 e B.1.617.2.
Analisi strutturale e funzionale degli anticorpi
Le analisi microscopiche crioelettrografiche di strutture complesse anticorpo-antigene hanno rivelato che due anticorpi con la più alta potenza di neutralizzazione si legano alla proteina spike con tutti i RBD in “posizione up”. Ulteriori analisi strutturali hanno rivelato che le modalità di legame epitopico degli anticorpi sono responsabili di un’elevata potenza neutralizzante contro i COV SARS-CoV-2. La capacità di legame e neutralizzazione degli anticorpi è stata influenzata negativamente da tre mutazioni spike, tra cui F486R, N487R e Y489R.
Resistenza agli anticorpi
La pressione di selezione degli anticorpi è stata applicata al ceppo WA-1 per identificare potenziali mutazioni di fuga che possono comparire durante l’infezione virale. La pressione di selezione positiva è stata applicata incubando il virus con concentrazioni crescenti di anticorpi per innescare la resistenza anticorpale.
In due degli anticorpi più potenti, uno è stato influenzato negativamente da una singola mutazione F486S e l’altro è stato influenzato dalle mutazioni F486L, N487D e Q493R. Tuttavia, la mutazione Q493R ha mostrato un impatto trascurabile sul legame e sulla neutralizzazione. Ulteriori analisi hanno rivelato che queste mutazioni di fuga sono principalmente assenti nelle varianti virali circolanti, indicando l’assenza di pressione di selezione.
Conducendo più cicli di selezione utilizzando trattamenti combinati con due anticorpi, è stato osservato che le combinazioni di anticorpi potrebbero ridurre il rischio di acquisizione di mutazioni di fuga e il successivo sviluppo di varianti virali resistenti.